RMC計算用プログラム
目次
はじめに
SPring8やJ-PARCで実験を行って構造因子を取得したら、Reverse Monte Carlo 法(RMC)を使って分子構造を評価します。O氏が姫路で遊んでいる間と新幹線の 移動中にRMC計算用のプリポストプログラムを作成しました。学内からのみプ ログラムをダウンロードできます。
- Version 2023.1用に修正しました。(17-Apr-2023)
- 複数データのフィット等、いくつかのプログラムをupdateしました。(20-Apr-2020)
- O氏に関連する文章を修正しました。 (27-Nov-2021)
測定データの確認
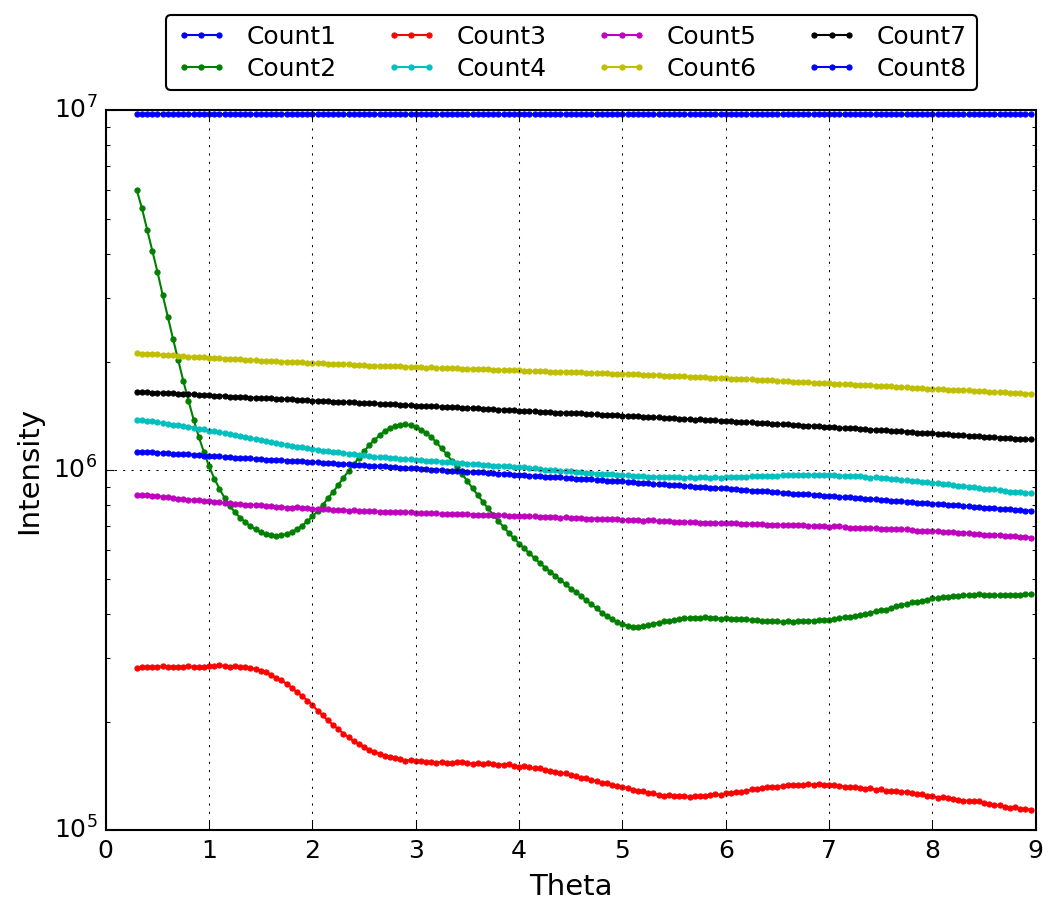
rmc_datplot.py
rmc_dat2interpolate.py
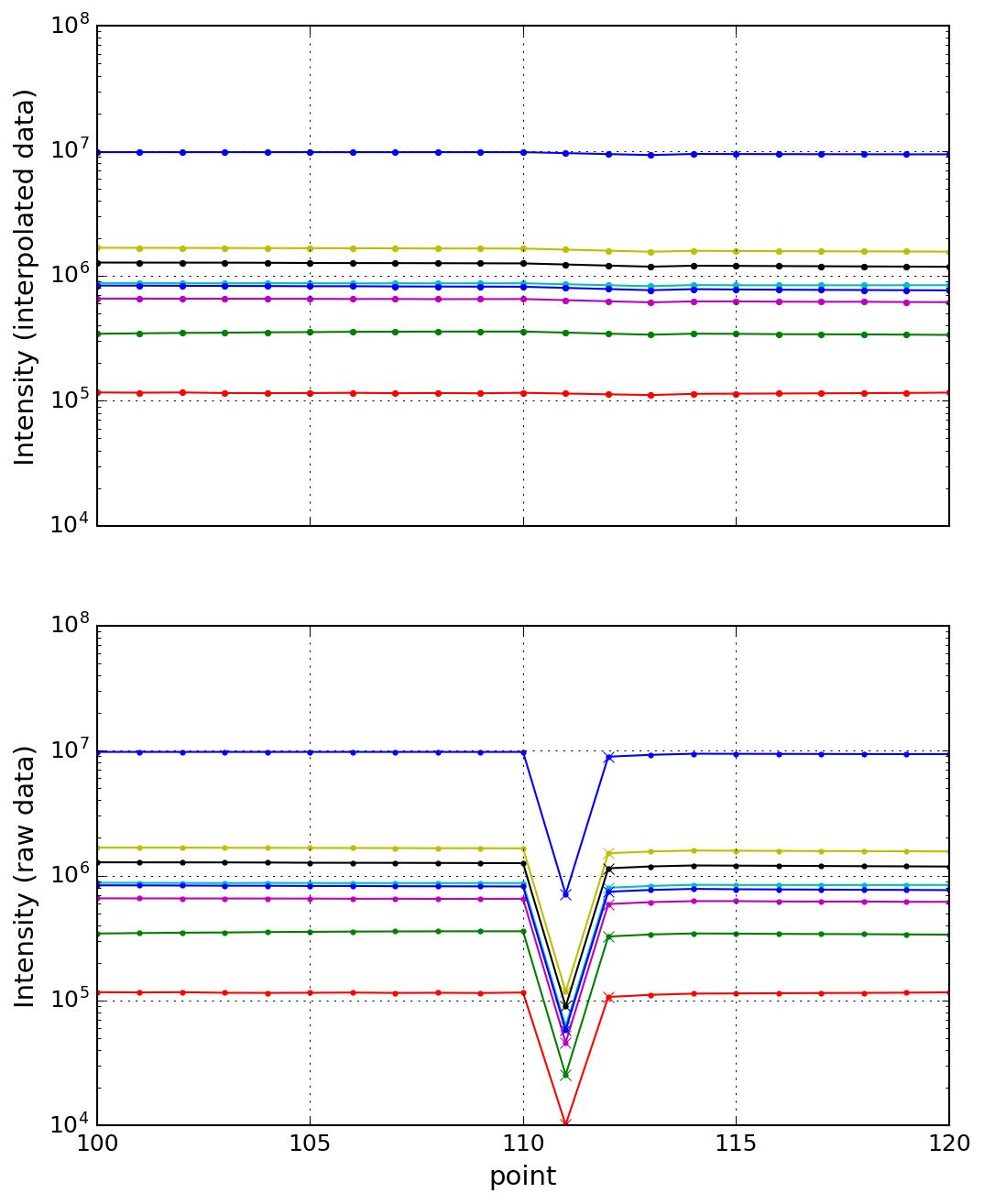
ビームが落ちた等で強度が妙なデータを前後のポイントで内挿して補完するプ ログラムです。補完するポイントと補完のための前後のポイント数を指定しま す。100-200のデータを表示して、111と112のポイントを106-110と113-117の ポイントで内挿して補完する例です。
rmc_dat2interpolate.py -x 100 200 -p 111 112 -s 5 04A_altered-2.dat -xl 100 120
補完したデータは、04A_altered-2_interp.datに保存されます。
04A_altered-2_interp.dat was created. 04A_altered-2_interp.png was created.
RMC用のインプットファイル作成
古典MDで構造をつくって、BL02B2で測定した散乱因子からインプットファイ ルを作成します。手順は以下のとおり。
- 古典MDで作成した原子構造(lammpstrj)からrmc用のcfgファイルを作成 (rmc_dump2cfg.py)
- 原子の数とセルサイズから原子を格子上にランダムに置いたrmc用のcfgファ イルを作成(rmc_makecfg.py)
- 実験データをrmc用のフォーマットに変換 (rmc_cfg2sq.py)
- rmc用のインプットファイルの作成(rmc_cfg2dat.py)
古典MDで構造が作れない場合は、rmc_makecfg.pyでランダムな初期構造kを作る。
rmc_convert2cfg.py
lammpstrjまたはxyz形式のデータをcfg形式に変換します。
rmc_dump2cfg.py 00A.lammpstrj
単位胞のサイズや原子種、原子座標の入った00A.cfgが生成されます。 xyzファイルの場合は、2行目にセルサイズを含む必要があります。
rmc_makecfg.py
rmc_cfg2sq.py
引数にcfgファイルと実験から求めたS(Q)のファイルを渡します。
rmc_cfg2sq.py -c 00A.cfg -s Sq_00A_pristine.txt
原子散乱因子を含むrmc用の00A_xrdraw.sqが生成されます。
rmc_cfg2dat.py
rmcのインプットファイルを作成します。引数にcfgファイルとrmc_cfg2sq.py で作成したS(Q)のファイルを渡します。
rmc_cfg2dat.py -c 00A.cfg -s 00A_xrdraw.sq
計算条件の00A.datが生成されます。このファイルを編集して束縛条件等の原 子を動かす条件を付け加えます。
計算の実行
作成したインプットファイルで正しくrmcが動作するか確認するために、1ステッ プのrmc計算を流します。
rmcp_onestep 00A
logファイルを見て、指定した通りの束縛条件になっているか確認します。指 定したとおりに実行できていたら、rmcを実行します。teeで標準出力に結果を 表示しつつ、標準出力を00A.logに保存します。00A.logは収束状況を確認する 時に使います。
rmcp 00A | tee 00A.log
ポスト処理
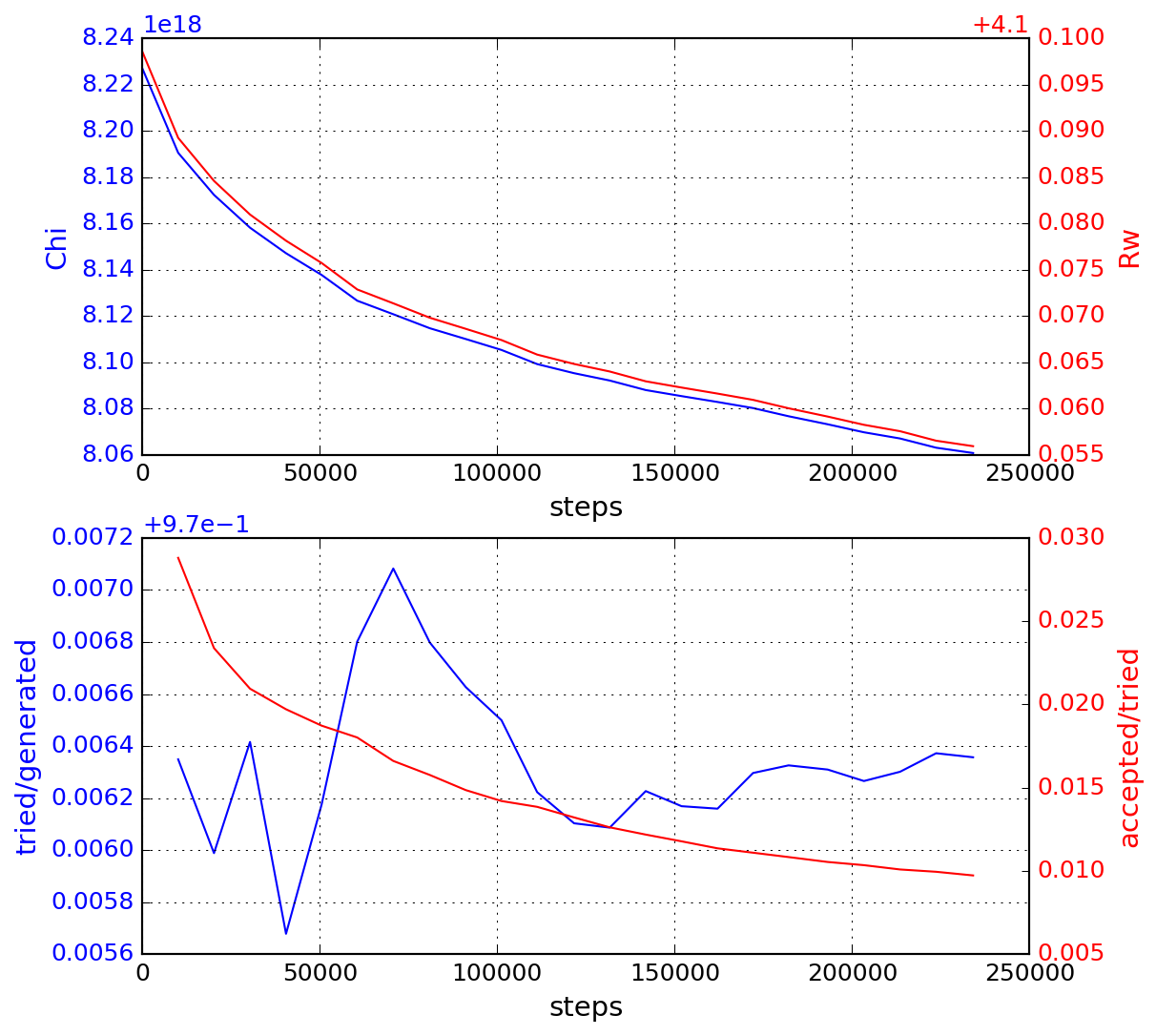
計算を流しながら、rmcが生成するファイルから収束状況やフィッテングの具 合、構造の妥当性をチェックします。計算結果を確認するためのポスト処理プ ログラムを作成しています。
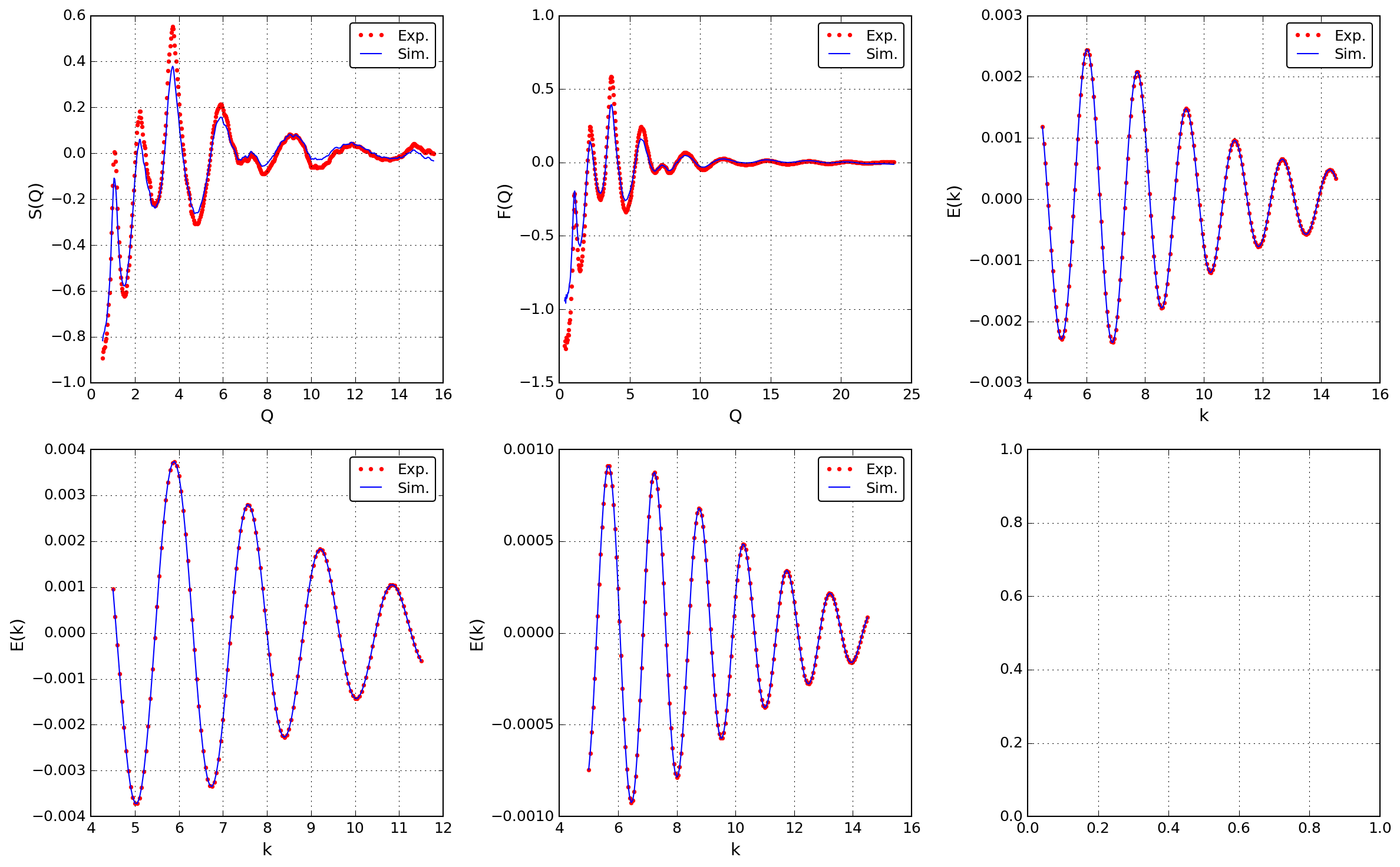
rmc_fitplot.py
rmc_logplot.py
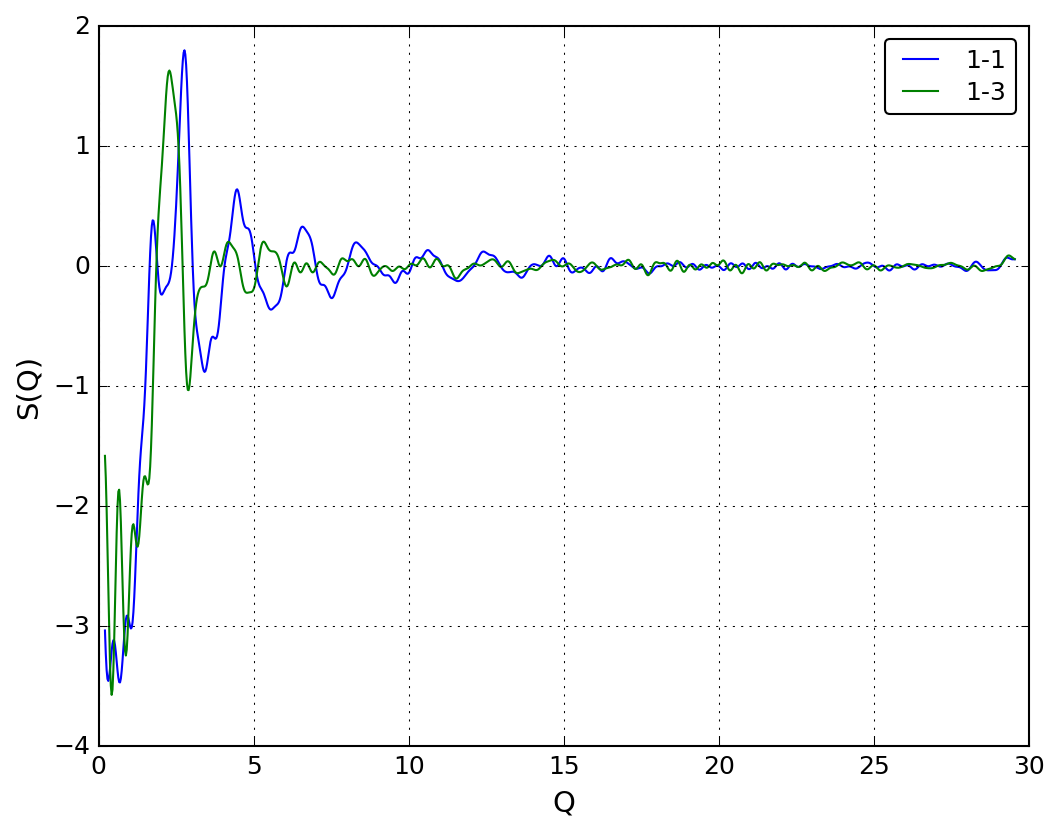
rmc_pfqplot.py
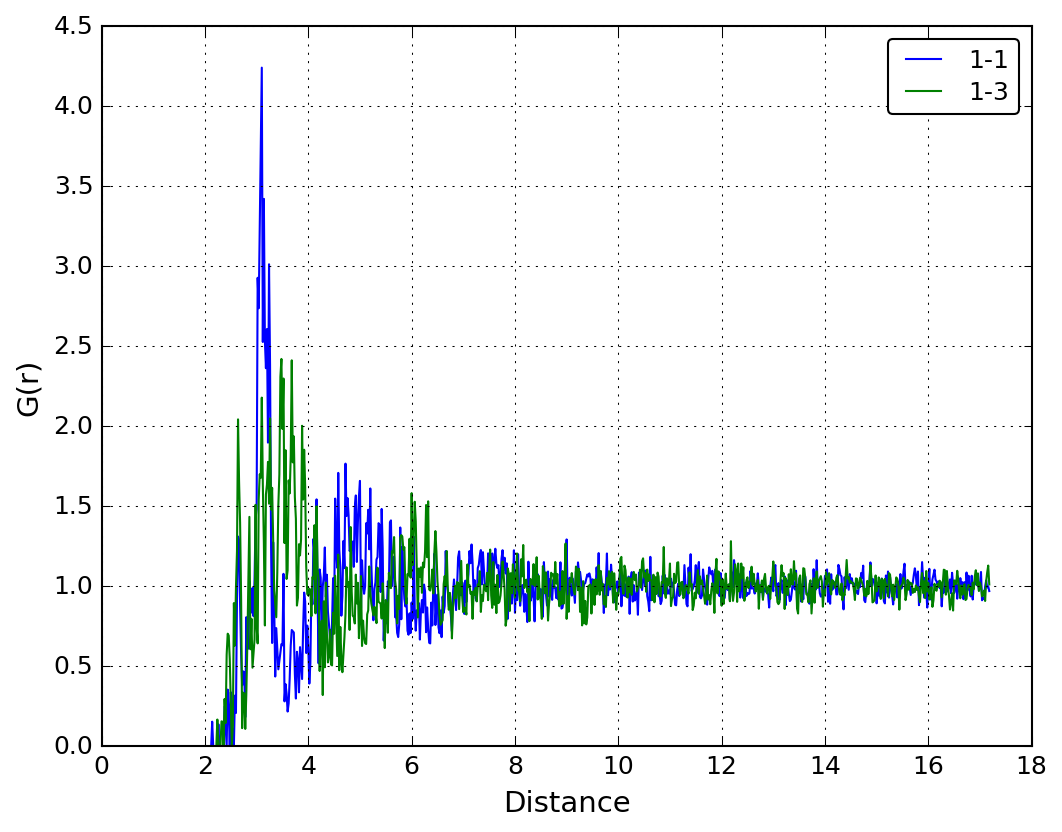
rmc_ppcfplot.py
rmc_cncheck.py
原子ペアとカットオフ距離から配位数分布をcfgファイルから求めます。引数 でcfgファイルの原子の並びを指定します。配位数を判定するための距離は、 rmc_check.pyの中で、以下のように辞書変数として直接指定しています。辞 書変数のキーが配位の種類、値が配位数をカウントする最小と最大距離で す。'O-Si,B,Al'の指定は、Oに対して、Si,B,Alの配位数をカウントするよう 指定しています。
CUTOFF['Si-O'] = [[1.0, 2.1]] CUTOFF['B-O'] = [[1.0, 2.1]] CUTOFF['Al-O'] = [[1.0, 2.3]] CUTOFF['O-Si,B,Al'] = [[1.0, 2.1], [1.0, 2.1], [1.0, 2.3]]
プログラム中で指定したCUTOFF全てのペアについて配位数をカウントします。 配位数を計算するペアを追加したければ、rmc_check.pyの中にCUTOFFを追加 すれば良いでしょう。CUTOFFで指定した原子がcfg中に存在しない場合、エラー になります。解析毎にrmc_cncheck.pyを作成して解析すれば良いでしょう。
実行例です。
rmc_cncheck.py 00A.cfg -e Si B Na O
標準出力に結果が表示されます。
Counting Si-O [[1.0, 2.1]]... ---------------------------------------- [cn]: N(%) Si for O ---------------------------------------- [3]: 26(3.8%) [4]: 638(94.1%) [5]: 14(2.1%) Counting B-O [[1.0, 2.1]]... ---------------------------------------- [cn]: N(%) B for O ---------------------------------------- [2]: 11(3.1%) [3]: 180(50.0%) [4]: 168(46.7%) [5]: 1(0.3%) Counting O-Si,B [[1.0, 2.1], [1.0, 2.3]]... ---------------------------------------- [cn]: N(%) O for Si,B ---------------------------------------- [0]: 3(0.1%) [1]: 154(7.6%) [2]: 1823(89.5%) [3]: 58(2.8%)
定義した辞書変数CUTOFF毎に配位数の数割合が表示されます。
rmc_cfg2convert.py
rmcのcfgファイルを各種フォーマットに変換します。cfgのデータに並びにした がった元素名を-eで指定する必要があります。-t で出力するフォーマットを 選べます。
rmc_cfg2convert.py hoge.cfg -e Si B O -t cif
指定できる出力フォーマットは、lammpstrj, cif, xyzです。
rmc_clean
中間ファイル一式を削除します。rmcpが生成するファイルをすべて削除する ので注意が必要です。